Olá Fernanda obrigado pela ajuda! Eu tinha pensando em regex anteriormente e não funcionou. Vou postar o meu código quem sabe não consiga me ajudar! De qualquer forma, lhe agradeço pela atenção!
Render.R
dados = read.xlsx(“C:\Users\RibeiroF\OneDrive - xxx\Francisco\Área de Trabalho\Atividades\Agro\Coc Agro\dados.xlsx”)
purrr::walk(
.x = dados$amostras,
~ rmarkdown::render(
input = “index.Rmd”,
output_file = glue::glue(“Coc Agro - {.x}.pdf”),
params = list(amostras = {.x})
)
)
Index.Rmd
title: "xxx - r params$amostras "
author: “xxx”
date: “2023-05-03”
format:
pdf:
papersize: A3
latex_engine: tinytex
classoption: landscape
execute:
echo: false
df-print: kable
editor: visual
params:
amostras: amostras
geometry: “a3paper,left = 1.5cm, right = 1.5cm, top=2cm, bottom=4cm, landscape”
header-includes:
- \usepackage{booktabs}
- \usepackage{longtable}
- \usepackage{array}
- \usepackage{multirow}
- \usepackage{wrapfig}
- \usepackage{float}
- \usepackage{colortbl}
- \usepackage{tabu}
- \usepackage{threeparttable}
- \usepackage{threeparttablex}
- \usepackage[normalem]{ulem}
- \usepackage{makecell}
- \usepackage{xcolor}
- \usepackage{fancyhdr}
- \usepackage{pdflscape}
- \usepackage{lastpage}
- \usepackage[labelformat = empty]{caption}
- \pagestyle{fancy}
- \fancyhf{}
- \fancyhead[LE,RO]{\thepage\ de \pageref{LastPage}}
- \fancyfoot[LE,LO]{Bloco1 - Al, Ba, B, Cu, Fe, Si, Zn, Sb, As, Be, Cd, Pb, Co, Cr, Sn, Li, Mn, Ni, Hg, Mo, Ag, Se, Tl, Ti, U, V, Bloco2 - Ca, S, P, Mg, K, Na, Bloco3 - Tolueno, etilbenzeno, diclorometano, Bloco4 - Aldrin, Endrin, Dieldrin, HCHtotal, HCHgama/lindano, PCBs, Bloco5 - 2,4,5-triclorofenol e 2,4,6-triclorofenol, Bloco7 - As, Hg e Cr total, Bloco8 - Cr (III), Cr (VI), Bloco9 - As (III), As (V), Ácido monometilarsônico, Ácido dimetilarsínico e Arsenobetaína, Bloco9 - Atrazina e Clorpirifós}
- \fancyfoot[C]{}
- \renewcommand{\footrulewidth}{0.25mm}
dados = read.xlsx("C:\\Users\\RibeiroF\\OneDrive - xxx\\Francisco\\Área de Trabalho\\Atividades\\Agro\\Coc Agro\\dados.xlsx")
dados = dados %>%
clean_names()%>%
mutate(data = as.numeric(data),
data = as.Date(data, format = "%d/%m/%Y", origin = "30/12/1899"),
hora = as.numeric(hora),
hora = as.times(hora, format = "h:m"))
|
|
| Empresa contratante: xxx |
Gestores responsáveis: xxx |
| Empresa responsável pela coleta e execução das análises: xxx |
Gestor responsavel: xxx |
ponto = dados%>%
dplyr::filter(amostras == params$amostras)%>%
dplyr::select(amostras)%>%
dplyr::distinct()%>%
dplyr::mutate(ponto = "")%>%
dplyr::mutate(ponto = str_extract(amostras, "[A-Z]{2}-[0-9]{4}"))%>%
dplyr::select(ponto)%>%
pull
amostra = dados%>%
dplyr::filter(amostras == params$amostras)%>%
dplyr::select(amostras)%>%
dplyr::distinct()%>%
pull
tipo = dados%>%
dplyr::filter(amostras == params$amostras)%>%
dplyr::select(amostras)%>%
dplyr::distinct()%>%
dplyr::mutate(tipo = "")%>%
dplyr::mutate(tipo = case_when(
str_detect(amostras, "T0")~ "Simples",
str_detect(amostras, "T1")~ "Simples",
str_detect(amostras, "T2")~ "Simples",
str_detect(amostras, "T3")~ "Simples",
str_detect(amostras, "TE")~ "Composta"))%>%
dplyr::select(tipo)%>%
pull
alimento = dados%>%
dplyr::filter(amostras == params$amostras)%>%
dplyr::select(amostras)%>%
dplyr::distinct()%>%
dplyr::mutate(alimento = "")%>%
dplyr::mutate(alimento = case_when(
str_detect(amostras, "FR01") ~ "Abacate",
str_detect(amostras, "FR02") ~ "Abacaxi",
str_detect(amostras, "FR03") ~ "Acerola",
str_detect(amostras, "FR04") ~ "Banana",
str_detect(amostras, "FR05") ~ "Cacau",
str_detect(amostras, "FR06") ~ "Cana-de-açúcar",
str_detect(amostras, "FR07") ~ "Coco-da-baía",
str_detect(amostras, "FR08") ~ "Goiaba",
str_detect(amostras, "FR09") ~ "Laranja",
str_detect(amostras, "FR10") ~ "Limão",
str_detect(amostras, "FR11") ~ "Mamão",
str_detect(amostras, "FR12") ~ "Manga",
str_detect(amostras, "FR13") ~ "Maracujá",
str_detect(amostras, "FR14") ~ "Melancia",
str_detect(amostras, "LE01") ~ "Abóbora",
str_detect(amostras, "LE02") ~ "Abobrinha",
str_detect(amostras, "LE03") ~ "Batata-inglesa",
str_detect(amostras, "LE04") ~ "Batata-doce",
str_detect(amostras, "LE05") ~ "Berinjela",
str_detect(amostras, "LE06") ~ "Beterraba",
str_detect(amostras, "LE07") ~ "Cenoura",
str_detect(amostras, "LE08") ~ "Chuchu",
str_detect(amostras, "LE09") ~ "Inhame",
str_detect(amostras, "LE10") ~ "Jiló",
str_detect(amostras, "LE11") ~ "Mandioca",
str_detect(amostras, "LE12") ~ "Pepino",
str_detect(amostras, "LE13") ~ "Pimentão",
str_detect(amostras, "LE14") ~ "Quiabo",
str_detect(amostras, "LE15") ~ "Tomate",
str_detect(amostras, "LE16") ~ "Vagem",
str_detect(amostras, "VE01") ~ "Alface",
str_detect(amostras, "VE02") ~ "Almeirão",
str_detect(amostras, "VE03") ~ "Couve",
str_detect(amostras, "VE04") ~ "Mostarda",
str_detect(amostras, "VE05") ~ "Repolho",
str_detect(amostras, "VE06") ~ "Agriao",
str_detect(amostras, "GR01") ~ "Café",
str_detect(amostras, "GR02") ~ "Feijão",
str_detect(amostras, "LT01") ~ "Vaca",
str_detect(amostras, "LT02") ~ "Cabra",
str_detect(amostras, "OV01") ~ "Galinha",
str_detect(amostras, "ME01") ~ "Mel",
str_detect(amostras, "MU01") ~ "Bovinos - Traseiro",
str_detect(amostras, "MU01") ~ "Bovinos - Traseiro",
str_detect(amostras, "MU02") ~ "Bovinos - Costela",
str_detect(amostras, "MU02") ~ "Bovinos - Costela",
str_detect(amostras, "MU03") ~ "Galinha - Coxa e sobrecoxa sem pele",
str_detect(amostras, "MU04") ~ "Galinha - Sobrecoxa com pele",
str_detect(amostras, "MU05") ~ "Suínos - Traseiro",
str_detect(amostras, "MU05") ~ "Suínos - Traseiro",
str_detect(amostras, "MU06") ~ "Suínos - Costela",
str_detect(amostras, "MU06") ~ "Suínos - Costela",
str_detect(amostras, "VI01") ~ "Coração de bovino",
str_detect(amostras, "VI02") ~ "Fígado de bovino",
str_detect(amostras, "VI03") ~ "Intestino de bovino",
str_detect(amostras, "VI04") ~ "Coração de galinha",
str_detect(amostras, "VI05") ~ "Fígado de galinha",
str_detect(amostras, "VI06") ~ "Moela de galinha"))%>%
dplyr::select(alimento)%>%
pull
grupo = dados%>%
dplyr::filter(amostras == params$amostras)%>%
dplyr::select(amostras)%>%
dplyr::distinct()%>%
dplyr::mutate(grupo = "")%>%
dplyr::mutate(grupo = case_when(
str_detect(amostras, "FR[0-9]{2}")~ "Fruto",
str_detect(amostras, "GR[0-9]{2}")~ "Grão",
str_detect(amostras, "LE[0-9]{2}")~ "Legume",
str_detect(amostras, "LT[0-9]{2}")~ "Leite",
str_detect(amostras, "ME[0-9]{2}")~ "Mel",
str_detect(amostras, "MU[0-9]{2}")~ "Músculo",
str_detect(amostras, "OV[0-9]{2}")~ "Ovo",
str_detect(amostras, "VE[0-9]{2}")~ "Verdura",
str_detect(amostras, "VI[0-9]{2}")~ "Viceras"))%>%
dplyr::select(grupo)%>%
pull
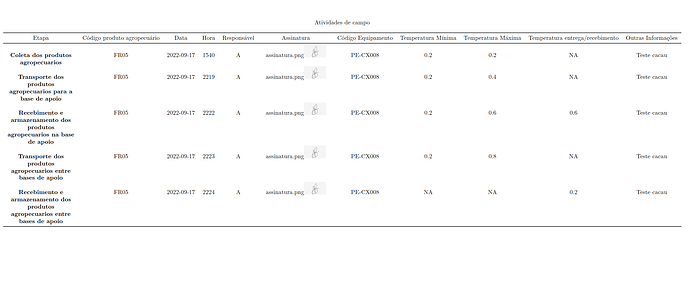
tabela_1 = dados %>%
dplyr::filter(amostras == params$amostras,
is.na(custodia),
etapa %in% c("Coleta dos produtos agropecuarios",
"Transporte dos produtos agropecuarios para a base de apoio",
"Recebimento e armazenamento dos produtos agropecuarios na base de apoio",
"Transporte dos produtos agropecuarios entre bases de apoio",
"Recebimento e armazenamento dos produtos agropecuarios entre bases de apoio"))%>%
dplyr::mutate(outras_informacoes = case_when(str_detect(amostras, "LE15")~ "Teste tomate",
str_detect(amostras, "FR05")~ "Teste cacau"))%>%
dplyr::mutate(amostras = str_extract(amostras, "[A-Z]{2}[0-9]{2}"))%>%
dplyr::select(-c(substancia, custodia))
nomes_colunas_tabela_1 = c("Etapa",
"Código produto agropecuário",
"Data",
"Hora",
"Responsável",
"Assinatura",
"Código Equipamento",
"Temperatura Mínima",
"Temperatura Máxima",
"Temperatura entrega/recebimento",
"Outras Informações")
tabela_2 = dados %>%
dplyr::filter(amostras == params$amostras,
is.na(custodia),
etapa %in% c("Entrega dos produtos agropecuarios para o transporte ate o laboratorio",
"Recebimento dos produtos agropecuarios para o transporte ate o laboratorio",
"Transporte dos produtos agropecuarios",
"Entrega dos produtos agropecuarios transportados",
"Recebimento dos produtos agropecuarios transportados",
"Cadastro e armazenamento dos produtos agropecuarios no laboratorio"))%>%
dplyr::mutate(outras_informacoes = case_when(str_detect(amostras, "LE15")~ "Teste tomate",
str_detect(amostras, "FR05")~ "Teste cacau"))%>%
dplyr::mutate(amostras = str_extract(amostras, "[A-Z]{2}[0-9]{2}"))%>%
dplyr::select(-c(substancia, custodia))
nomes_colunas_tabela_2 = c("Etapa",
"Código produto agropecuário",
"Data",
"Hora",
"Responsável",
"Assinatura",
"Código Equipamento",
"Temperatura Mínima",
"Temperatura Máxima",
"Temperatura entrega/recebimento",
"Outras Informações")
tabela_3 = dados %>%
dplyr::filter(amostras == params$amostras,
is.na(custodia),
etapa %in% c("Geracao de amostra e armazenamento",
"Geracao de contraprova e armazenamento",
"Liofilizacao da amostra e armazenamento",
"Preparo da amostra e armazenamento",
"Analise da amostra",
"Descarte da amostra"))%>%
dplyr::mutate(outras_informacoes = case_when(str_detect(amostras, "LE15")~ "Teste tomate",
str_detect(amostras, "FR05")~ "Teste cacau"))%>%
dplyr::select(-c(amostras, custodia))
nomes_colunas_tabela_3 = c("Etapa",
"Substância Química",
"Data",
"Hora",
"Responsável",
"Assinatura",
"Código Equipamento",
"Temperatura Mínima",
"Temperatura Máxima",
"Temperatura entrega/recebimento",
"Outras Informações")
tabela_4 = dados %>%
dplyr::filter(amostras == params$amostras,
custodia == "Bioagri",
etapa %in% c("Geracao de amostra e armazenamento",
"Geracao de contraprova e armazenamento",
"Liofilizacao da amostra e armazenamento",
"Preparo da amostra e armazenamento",
"Analise da amostra",
"Descarte da amostra"))%>%
dplyr::mutate(outras_informacoes = case_when(str_detect(amostras, "LE15")~ "Teste tomate",
str_detect(amostras, "FR05")~ "Teste cacau"))%>%
dplyr::select(-c(amostras, custodia))
nomes_colunas_tabela_4 = c("Etapa",
"Substância Química",
"Data",
"Hora",
"Responsável",
"Assinatura",
"Código Equipamento",
"Temperatura Mínima",
"Temperatura Máxima",
"Temperatura entrega/recebimento",
"Outras Informações")
tabela_5 = dados %>%
dplyr::filter(amostras == params$amostras,
custodia == "CQA",
etapa %in% c("Geracao de amostra e armazenamento",
"Geracao de contraprova e armazenamento",
"Liofilizacao da amostra e armazenamento",
"Preparo da amostra e armazenamento",
"Analise da amostra",
"Descarte da amostra"))%>%
dplyr::mutate(outras_informacoes = case_when(str_detect(amostras, "LE15")~ "Teste tomate",
str_detect(amostras, "FR05")~ "Teste cacau"))%>%
dplyr::select(-c(amostras, custodia))
nomes_colunas_tabela_5 = c("Etapa",
"Substância Química",
"Data",
"Hora",
"Responsável",
"Assinatura",
"Código Equipamento",
"Temperatura Mínima",
"Temperatura Máxima",
"Temperatura entrega/recebimento",
"Outras Informações")
Informações da Amostra
Amostra: r amostra
Ponto: r ponto
Tipo: r tipo
Alimento: r alimento
Grupo: r grupo
tabela_1 = kableExtra::kbl (tabela_1, caption = "Atividades de campo", booktabs = T, longtable = T,
col.names = nomes_colunas_tabela_1, align = "c")%>%
kable_styling(font_size = 10, latex_options = c("repeat_header", "HOLD_position"), position = "center")%>%
column_spec (1, bold = T, width = "4cm")%>%
column_spec (6, width = "4cm", image = spec_image(tabela_1$assinatura, 150, 150))
r tabela_1
tabela_2 = kableExtra::kbl (tabela_2, caption = "Transporte dos produtos agropecuarios e recebimento em laboratorio", booktabs = T, longtable = T,
col.names = nomes_colunas_tabela_2, align = "c")%>%
kable_styling(font_size = 10, latex_options = c("repeat_header", "HOLD_position"), position = "center")%>%
column_spec (1, bold = T, width = "4cm")%>%
column_spec (6, width = "4cm", image = spec_image(tabela_2$assinatura, 150, 150))
r tabela_2
tabela_3 = kableExtra::kbl (tabela_3, caption = "Atividades em laboratorio", booktabs = T, longtable = T,
col.names = nomes_colunas_tabela_3, align = "c")%>%
kable_styling(font_size = 10, latex_options = c("repeat_header", "HOLD_position"), position = "center")%>%
column_spec (1, bold = T, width = "4cm")%>%
column_spec (6, width = "4cm", image = spec_image(tabela_3$assinatura, 150, 150))
r tabela_3
tabela_4 = kableExtra::kbl (tabela_4, caption = "Análises Bioagri", booktabs = T, longtable = T,
col.names = nomes_colunas_tabela_4, align = "c")%>%
kable_styling(font_size = 10, latex_options = c("repeat_header", "HOLD_position"), position = "center")%>%
column_spec (1, bold = T, width = "4cm")%>%
column_spec (6, width = "4cm", image = spec_image(tabela_4$assinatura, 150, 150))
r tabela_4
tabela_5 = kableExtra::kbl (tabela_5, caption = "Análises CQA", booktabs = T, longtable = T,
col.names = nomes_colunas_tabela_5, align = "c")%>%
kable_styling(font_size = 10, latex_options = c("repeat_header", "HOLD_position"), position = "center")%>%
column_spec (1, bold = T, width = "4cm")%>%
column_spec (6, width = "4cm", image = spec_image(tabela_5$assinatura, 150, 150))
r tabela_5
Eu gostaria de remover da coluna Assinatura, o “assinatura.png”, “teste.png”…